DNA情報を98%圧縮し、作物の性質を高精度予測
―AIにより計算時間を大幅短縮、品種改良を加速―
【注目の成果:共同研究・産学連携のためのチェックポイント】
 | DNA情報から作物の性質を迅速に予測し、有望な品種を効率的に選抜することが可能になります。これにより、品種改良の高速化とコスト削減が期待 |
【産学連携対象 全学共通分野 Discovery Saga】
【Sagaキーワード】
データ管理/データ圧縮/データ駆動/AI/ニューラルネットワーク/畳み込みニューラルネットワーク/深層学習/人工知能(AI)/Lasso/遺伝情報/持続可能/サポートベクターマシン/データ処理/ニューラルネット/トウモロコシ/病害抵抗性/環境ストレス/イネ/抵抗性/ベクター/スクリーニング/ゲノム/ストレス
発表のポイント
◆数百万〜1,000万以上の遺伝マーカーを含むゲノムデータを、最大98%圧縮しても高い予測精度を維持する手法を開発しました。◆データ圧縮により、計算時間とデータ保存コストを大幅に削減しました。
◆イネおよびトウモロコシのデータで、従来手法よりも高い予測精度を達成しました。
◆DNA情報から有望な品種を効率的に選びだす技術として、品種改良の加速に貢献します。
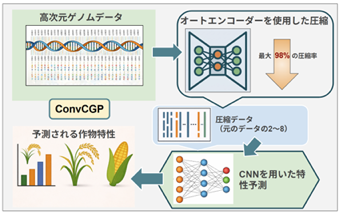 本研究の概要
本研究の概要膨大なDNA情報をAIで圧縮し、その圧縮データから作物の性質(収量や草丈など)を予測することで、有望な品種の選抜を効率化する。
発表概要
東京大学大学院農学生命科学研究科の雷帆タンジラ特任助教と岩田洋佳教授らの研究グループは、作物のゲノムデータを大幅に圧縮しながら、収量や草丈などの性質を高精度に予測できる新しい深層学習手法「ConvCGP」を開発しました。近年の品種改良では、数百万から1,000万以上の遺伝マーカーを含むゲノムデータを用いて、作物の性質を予測する「ゲノミック予測」が活用されています。しかし、データの大規模化により、計算時間やデータ保存の負担が大きな課題となっていました。
本研究では、重要な遺伝情報を保ったままデータを圧縮し、その圧縮データから作物の性質を予測する手法を開発しました。その結果、元のデータのわずか2%程度に圧縮しても高い予測精度を維持できることを示しました。
発表内容
背景品種改良では、収量や品質、環境ストレスへの耐性などに優れた品種を効率的に選ぶことが重要です。近年は、DNA情報(ゲノムデータ)をもとに作物の性質を予測する「ゲノミック予測1)」が広く用いられており、実際に栽培する前の段階で有望な個体を選抜できるようになっています。これにより、品種改良の期間短縮と効率化が進んでいます。
一方で、ゲノミック予測では、数百万から1,000万以上の遺伝マーカーを含むゲノムデータ2)を扱うため、計算時間やデータ管理の負担が大きく、特に大規模な育種プログラムにおいて課題となっていました。
研究成果の内容
本研究では、この課題を解決するため、深層学習3)を用いた新しい手法「ConvCGP」を開発しました。本手法は、まずオートエンコーダによってゲノムデータを圧縮し、その後、畳み込みニューラルネットワーク(CNN)によって作物の性質を予測する二段階の構造を持ちます。これにより、重要な遺伝情報を保持したまま、効率的な予測が可能となります。
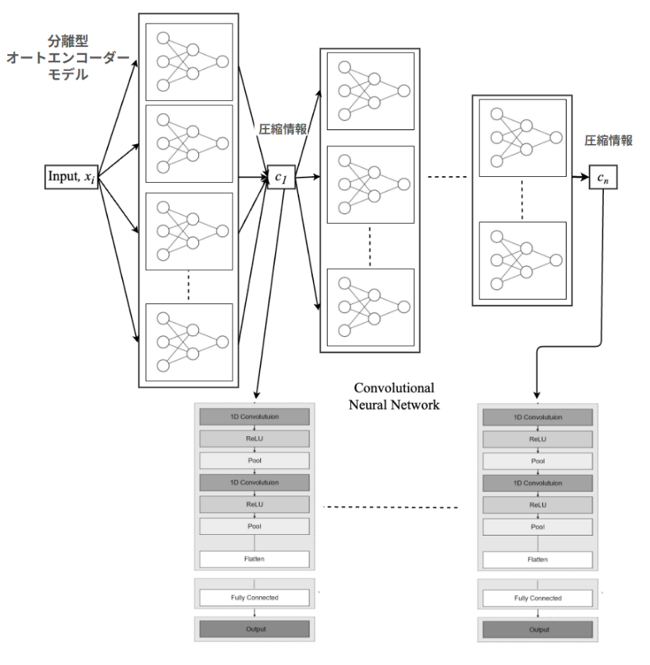 図1:提案手法「ConvCGP」の概要
図1:提案手法「ConvCGP」の概要ゲノムデータをAIで圧縮(オートエンコーダ)し、その圧縮データからAI(CNN)によって作物の性質を予測する二段階の手法。
イネおよびトウモロコシの大規模データを用いた検証では、データを93〜98%圧縮(元データの2〜7%)しても、高い予測精度を維持できることが確認されました。特に、約70万マーカーのイネデータや約1,170万マーカーのトウモロコシデータにおいても、圧縮後のデータから高精度な予測が可能でした。
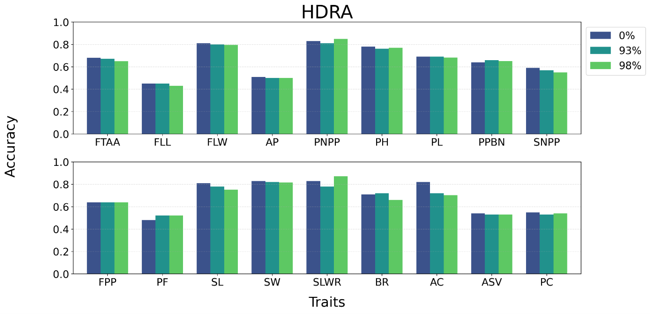 図2:ゲノムデータ圧縮後の予測精度(イネ)
図2:ゲノムデータ圧縮後の予測精度(イネ)ゲノムデータを最大98%圧縮しても、収量や草丈などの性質の予測精度がほぼ維持されることを示す。
FTAA:アーカンソーにおける出穂期, FLL:止葉長, FLW:止葉幅, AP:芒の有無, PNPP:株当たり穂数, PH:稈長, PL:穂長, PPBN:一次枝梗数, SNPP:穂当たり粒数, FPP:穂当たり小花数, PF:稔実率, SL:粒長, SW:粒幅, SLWR:粒長幅比, BR:いもち病抵抗性, AC:アミロース含量, ASV:アルカリ崩壊値, PC:タンパク質含量
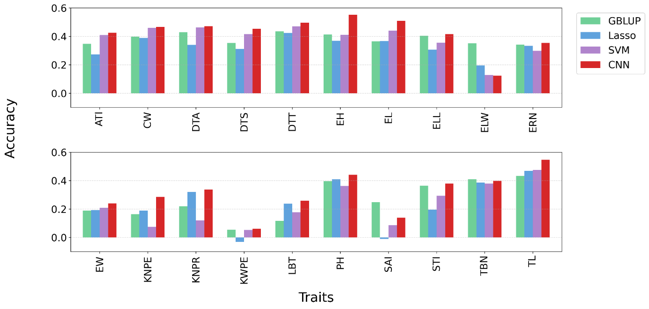 図3:従来手法との予測精度の比較(トウモロコシ)
図3:従来手法との予測精度の比較(トウモロコシ)ConvCGPは、GBLUPやLassoなどの従来手法と比べ、多くの性質において高い予測精度を示す。
ATI:葯–雄穂間隔, CW:穂芯重, DTA:雄穂開花日数, DTS:絹糸抽出日数, DTT:雄穂出穂日数, EH:着雌穂高, EL:穂長, ELL:穂位葉長, ELW:穂位葉幅, ERN:穂列数, EW:穂重, KNPE:穂当たり粒数, KNPR:列当たり粒数, KWPE:穂当たり粒重, LBT:不稔先端長, PH:草丈, SAI:絹糸–葯間隔, STI:絹糸–雄穂間隔, TBN:雄穂分枝数, TL:雄穂長
また、計算効率も大幅に向上しました。例えば、イネのデータでは予測に要する時間が約2分50秒から約14秒へ短縮され、大規模データでは1日以上かかっていた計算が数十分程度まで短縮されました。
さらに、GBLUPやLasso、サポートベクターマシンなどの従来手法と比較して、多くの性質においてより高い予測精度を示しました。開花時期や草丈、病害抵抗性など、複雑な遺伝的背景を持つ性質に対しても安定した予測が可能であることが確認されました。 本手法は圧縮率を用途に応じて調整できるため、大規模スクリーニングから精密な品種設計まで柔軟に対応できます。
社会的意義・今後の展開
本研究で開発された技術により、DNA情報から作物の性質を迅速に予測し、有望な品種を効率的に選抜することが可能になります。これにより、品種改良の高速化とコスト削減が期待されます。また、本技術はデータ処理に伴う計算資源の削減にもつながるため、データ駆動型農業の効率化や持続可能な農業(GX:グリーントランスフォーメーション)の推進にも貢献すると期待されます。今後は、環境データとの統合や他作物への応用を進めることで、より高度な予測と実用化を目指します。
発表者・研究者等情報
東京大学 大学院農学生命科学研究科雷帆 タンジラ 特任助教(Tanzila Islam)
岩田 洋佳 教授(Hiroyoshi Iwata)
岩手大学
理工学部
金 天海 准教授(研究当時)(Chyon Hae Kim)
農学部・次世代アグリイノベーション研究センター
下野 裕之 教授 (Hiroyuki Shimono)
理工学部・次世代アグリイノベーション研究センター
木村 彰男 教授 (Akio Kimura)
論文情報
雑誌名:The Plant Genome題 名:ConvCGP: A Convolutional Neural Network to Predict Genetic Values of Agronomic Traits from Compressed Genome-wide Polymorphisms
著者名:Tanzila Raihan, Chyon Hae Kim, Hiroyuki Shimono, Akio Kimura, Hiroyoshi Iwata
DOI:https://doi.org/10.1002/tpg2.70223
研究助成
本研究は、JSPS科研費(JP19H00938、JP22H02306)およびJST AI-ENGENEプログラム(JPMJMS25E3)の支援を受けて実施されました。用語解説
1)ゲノミック予測:DNA情報(ゲノムデータ)をもとに、作物の性質(収量や草丈など)を予測する手法。2)ゲノムデータ:DNA上の多数の遺伝マーカーの情報。作物では数百万から1,000万以上のマーカーが利用される。
3)深層学習:データの特徴を自動的に学習する人工知能の一種。本研究では、データ圧縮と性質の予測に用いられる。
問い合わせ先
<研究内容について>東京大学 大学院農学生命科学研究科
教授 岩田 洋佳 (いわた ひろよし)
E-mail:hiroiwata@g.ecc.u-tokyo.ac.jp
<機関窓口>
東京大学大学院農学生命科学研究科・農学部
総務課総務チーム広報情報担当
Tel:03-5841-5484 E-mail:koho.a@gs.mail.u-tokyo.ac.jp
 東京大学 研究
東京大学 研究